
DETECCION Y MODELADO DE GENES
2 ESTRATEGIA GENERAL Y METODOS DE PREDICCION
Independientemente de si la predicción de genes se realiza a
pequeña escala o a escala genómica, o de si se realiza utilizando
programas individuales con diferentes funcionalidades, o utilizando un
sistema integrado, los siguientes metodos generales se aplican de forma
consistente:
Localización y enmascaramiento de secuencias repetidas.
Métodos de comparación (métodos Extrínsecos
o Comparative methods).
Análisis de la secuencia de ADN a nivel de nucleótido
(Content-based methods).
Análisis de señales o motivos (Signal-based methods).
Busqueda en bases de datos de secuencias expresadas.
Localización y enmascaramiento
de secuencias repetidas
Especialmente en el caso de genomas
eucariotas, la primera fase del proceso de predicción de genes es
localizar zonas de secuencias repetidas, en las que es poco probable encontrar
elementos reguladores y secuencias codificantes. Las zonas de secuencias
repetidas pueden ser entonces descartadas a la hora de ejecutar otros tipos
de análisis, o enmascaradas, mediante la sustitución de los
caracteres que representan los cuatro nucleótidos por otro símbolo
arbitrario, por ejemplo "N" o "X".
Además de servir para descartar regiones
de menor interés desde el punto de vista funcional, el enmascaramiento
de secuencias repetidas facilita la búsqueda de secuencias similares
en bases de datos de secuencias con, por ejemplo, programas de la familia
de aplicaciones BLAST.
Normalmente, el enmascaramiento es realizado
de forma automática por muchos programas. En BLASTN,
por ejemplo, el usuario puede seleccionar distintos tipos de filtro,
aunque la opción por defecto enmascara las denominadas regiones
de baja complejidad mediante un programa llamado DUST. Otras opciones en
BLASTN
permiten enmascarar secuencias repetidas humanas (LINEs y SINEs) o secuencias
especificadas por el usuario, mediante el uso de minúsculas, en
la secuencia usada como "query".
Uno de los programas más usados
para enmascarar secuencias repetidas en secuencias de mamíferos
es RepeatMasker,
que filtra tanto regiones de baja complejidad, como aquellas secuencias
identificadas por su similaridad a las de una base de datos de secuencias
repetidas, RepBase,
mantenida por el Genetic Information Research Institute (GIRI).
En promedio, el 50% de cualquier secuencia genómica humana sería
reconocido como secuencias repetidas, y enmascarado, por RepeatMasker.
Métodos de comparación (métodos Extrínsecos
o Comparative methods)
La búsqueda de genes o de productos génicos
homólogos es uno de los métodos más antiguos y más
usados para identificar secuencias codificantes y determinar la estructura
de genes. Este tipo de métodos se califican como extrínsecos
porque se basan en usar información procedente del estudio de otros
genomas. Son, por tanto, menos eficientes en Eucariotas que en Procariotas
dada la menor abundancia de información de especies evolutivamente
cercanas.
La familia de aplicaciones BLAST
incluye programas que permiten hacer diferentes tipos de búsquedas.
-
BLASTN permitiria identificar genes parecidos en bases de datos de secuencias
de ADN, usando la secuencia genomica como "query".
-
BLASTX traduce la secuencia "query" en las seis fases de lectura posibles
y hace busquedas en bases de datos de proteinas; esto permitiria identificar
productos genicos parecidos a los codificados por la secuencia genomica,
y serviria para identificar regiones codificantes (no intrones).
-
TBLASTX traduce la secuencia "query" en las seis fases abiertas de lectura
y hace busquedas en bases de datos de secuencias de ADN tambien traducidas
en la seis fases de lectura posibles; esto serviria para identificar secuencias
que codifican para productos parecidos a los que codifica la secuencia
"query".
Si se conoce, o se puede predecir, la secuencia del producto genico,
o parte de ella, otros programas permiten usar la secuencia de aminoacidos
como "query":
-
BLASTP busca proteinas parecidas en bases de datos de proteinas.
-
TBLASTN hace busquedas en bases de datos de secuencias de ADN traducidas
en la seis fases de lectura posible.
El programa Procrustes
está diseñado para intentar deducir la estructura de un gen,
en cuanto a intrones y exones, basándose en la secuencia de aminoácidos
de una serie de proteínas homólogas a las que supone está
codificada por el fragmento de ADN que se está analizando. La secuencia
de dichas proteínas homólogas tiene que ser facilitada por
el usuario del programa, que podría haberlas identificado mediante
búsquedas con BLASTX, por ejemplo. Si la secuencia aminoacídica
facilitada es la que codifica el fragmento de ADN, Procrustes es capaz
de reconstruir la estructura del gen con un 99% de exactitud.
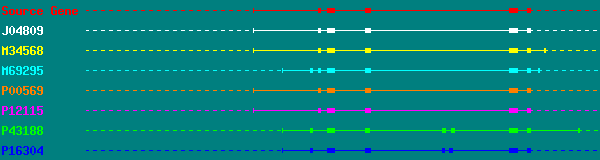
La figura de abajo es un ejemplo de resultado obtenido con Procrustes,
en el que proteinas homólogas de varios organismos han sido alineadas
con una secuencia genómica de ADN, para predecir la organización
de intrones y exones.
Análisis de secuencias de ADN a nivel de nucleótido
(Content-based methods).
Estos métodos se basan en el análisis de las propias
secuencias de ADN y son, por tanto, de tipo intrínseco (en
oposición a los métodos extrínsecos). Consisten
en el análisis estadístico de la composición del ADN,
muy frecuentemente para detectar sesgos en las frecuencias de trinucleótidos
impuestas por las restricciones que impone el código genético
en las zonas codificantes.
-
El contenido G+C es la medida más
simple. Aún así, puede ser de ayuda a la hora de deducir
la estructura de un gen dado que el contenido en G+C es más alto
en las 5'-UTR que en las 3'-UTR. Esta diferencia es especialmente marcada
en los vertebrados de sangre caliente.
-
El contenido en G+C de la tercera posición de los codones
de bacterias con alto contenido en G+C, como las del género Streptomyces,
puede ser de hasta un 92% (mientras que el contenido en G+C del genoma
de Streptomyces coelicolor, por ejemplo, es del 73%). Esta particularidad
es la usada por el programa FramePlot
para identificar regiones codificantes.
-
GC3s. Este parámetro es parecido al anterior y mide la
frecuencia de codones sinónimos en los que la tercera posición
es G o C.
-
Uso de Codones. Las frecuencias de uso de cada uno de los codones,
y las frecuencias de uso de codones sinónimos, pueden también
usarse para predecir si una secuencia es codificante o nó. Dado
que dichas frecuencias varían entre genomas y entre genes de un
mismo genoma, es necesario disponer de tablas de frecuencias específicas,
apropiadas para la secuencia que se vá a analizar. Existen muchos
programas para calcular tablas de de uso de codones a partir de secuencias
yá caracterizadas (por ejemplo el contenido en la Sequence
Manipulation Suite, que es accesible a traves de Internet), y también
pueden ser obtenidas de bases de datos especializadas (Codon
Usage Database).
-
Indice de Adaptación de Codones (CAI). Este parámetro
mide el grado en que el uso de codones de una secuencia se adapta a las
frecuencias de uso de codones calculadas previamente para un organismo,
o para un subconjunto de genes del mismo. Más que para predecir
la existencia de zonas de uso de codones, el CAI se usa para predecir el
nivel de expresión de un gen o para comparar el uso de codones entre
organismos. El programa CodonW
puede ser usado para calcular el CAI, asi como para realizar otros calculos
estadísticos relacionados con el uso de codones.
-
Otros parametros relacionadas con el uso de codones miden la frecuencia
en la que ocurren pares de codones sucesivos (dicodon counts), la
periodicidad de oligonucleótidos repetidos o la complejidad en la
composicón de nucleótidos.
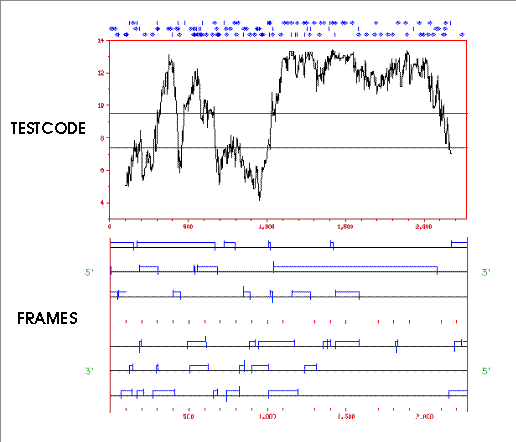
La figura adjunta ilustra un ejemplo de la aplicación
de este tipo de métodos, en el que dos programas del paquete GCG
de la Universidad de Wisconsin (ahora producido por Accelrys) se han utilizado
para analizar un fragmento genómico de Escherichia coli de
unos 2400 pb. En el panel superior se presenta el resultado obtenido con
TESTCODE, que representa gráficamente una medida de la falta de
aleatoriedad en cada tercer nucleótido, dentro de una ventana deslizante
de un cierto número de nucleótidos. La falta de aleatoriedad
en cada tercera posición es característica de secuencias
codificantes. El análisis indica que entre las posiciones 1000 y
2000, aproximadamente, existe una región con alta posibilidad de
ser codificante. Dicha región coincide con una fase abierta de lectura
predicha por FRAMES, visible en la segunda línea del panel inferior.
Análisis de señales o motivos (Signal-based
methods)
Al igual que el análisis estadístico de la composición
del ADN, el análisis de señales o motivos también
se considera un método de tipo intrínseco. Estos métodos
se basan en la identificación de motivos de secuencia característicos
de los elementos que forman parte de los genes, tales como promotores,
codones de inicio y terminación, sitios de procesamiento del ARN
(en Eucariotas), terminadores de transcripción (en Procariotas),
etc.
El grado de conservación de cualquiera de esos motivos varía
considerablemente. Aquellos relativamente conservados pueden ser identificados
mediante búsquedas con secuencias consenso, que representan
la secuencia del motivo para una cierta mayoría de ejemplos. Fuzznuc
es un ejemplo de programa para buscar ocurrencias de una secuencia consenso
en otra secuencia. El programa permite especificar el número de
fallos (mismatches) que serían aceptables, así como
utilizar secuencias consenso ambiguas (por ejemplo, [ACG] significa A,
C o G).
Las secuencias consenso (incluso las ambiguas) tienen el problema
de que no contienen información de la frecuencia con que cada nucleótido
ocurre en cada posición. Dicha información puede ser expresada,
sin embargo, en forma de perfiles (profiles o position
weight matrices, PWMs), que son tablas en las que se recoje
la frecuencia con que cada nucleótido aparece en cada posición
a lo largo de la secuencia.
Una aproximación parecida es la de los algoritmos que usan
modelos
ocultos de Markov (Hidden Markov Models, HMM).
Muchos de los programas desarrollados recientemente para detectar los límites
entre exones e intrones (ver sección
3) usan esta estrategia.
Búsqueda en bases de datos de secuencias expresadas
Estos metodos hacen uso de informacion proviniente de tecnicas
experimentales diseñadas para identificar productos genicos de forma
masiva. Dos ejemplos representativos de esta estrategia son el uso de bases
de datos de ESTs y de secuencias N-terminales de proteinas, que son utilizados
para confirmar la existencia de genes y para deducir la estructura
genica.
Los ESTs (Expressed Sequence Tags) son secuencias cortas de ADN (de
200 a 500 pb), generadas mediante la secuenciación de los extremos
5' y 3' de clones de ADNc seleccionados al azar. Los clones de ADNc se
obtienen, a su vez, por transcripción reversa de ARN mensajero obtenido
de una cierta fuente de células. Aunque los ADNc así obtenidos
suelen corresponder con fragmentos de ARN mensajeros, la secuenciación
de los extremos de los clones permite la identificación, de una
manera rápida, del repertorio de genes expresados en una cierta
condición, por un cierto tipo de células. Dado que las genotecas
de ADNc se obtienen a partir de ARN mensajero que ha sido ya procesado,
los ESTs corresponden a exones o a fragmentos de exones. Por tanto,
la identificación de ESTs que corresponden con fragmentos de una
secuencia de ADN genómico proporciona información sobre la
localización de genes y la organización de los exones e intrones.
La principal base de datos pública sobre ESTs es dbEST,
que es mantenida por el NCBI y que es, de hecho, una de las divisiones
de la base de datos GenBank.
Dicha base de datos almacena no sólo secuencias de ESTs, sino secuencias
de ADNc completos, cuyas secuencias pueden corresponder a la práctica
totalidad de los ARNm maduros que sirvieron de molde.
De acuerdo al inventario
de dbEST, el 15 de Marzo de 2002 había 11.018.340 entradas,
de las cuales 4.200.640 correspondían a ESTs humanos y 2.547.581
a ESTs de ratón. Las entradas de la base de datos pueden ser recuperadas
mediante búsquedas con palabras clave, desde la página principal
de dbEST. A la hora de
desarrollar el modelo de un gen, una secuencia genómica se puede
usar como "query" en búsquedas con BLASTN
restringidas a la base de datos de ESTs.
El EBI mantiene una página con enlaces a sitios web relacionados
con ESTs (EST
Links).
La identificacion de genes por busqueda en un base de datos de secuencias
N-terminales de proteinas fue utilizada para anotar el genoma de Escherichia
coli [Science 277:1453 (1999)].
Información adicional
Computational
Gene Identification. R.Guigó. Curso de Doctorado en Bioinformática.
UAM 2001.
Computational Gene Finding.
R. Guigó et al. Course 2001.
Finding
genes. Conceptos básicos sobre el uso de HMM para identificar
genes.
Protein
and DNA Hidden Markov Models. User's guide for HMMer. Sean Eddy. Washington
University.
Predictive methods using DNA sequences. A. D. Baxevanis. En "Bioinformatics.
A practical guide to the analysis of genes and proteins". Wiley-Interscience,
New York 2001.
Predictive methods using nucleotide sequences. J. W. Fickett. En "Bioinformatics.
A practical guide to the analysis of genes and proteins". Wiley-Interscience,
New York 1998.
Gene prediction tools. L. Milanesi e I. B. Rogozin. En "Protein sequence
analysis in the postgenomic era". CLUEB, Bologna 2001.
Recent developments and future directions in computational genomics.
S. Tsoka and C. A. Ouzonis. FEBS Letters 2000, 480:42.
Untranslated regions of mRNAs. F. Mignone et al. Genome Biology 2002,
3(3):reviews0004.1.
Páginas web de los distintos programas mencionados en, y enlazados
desde, esta misma página y desde esta
otra.



