Así como las herramientas que hemos visto hasta ahora iban principalmente encaminadas a predecir la función de nuestras secuencias, las comparaciones nos ofrecen informaciones adicionales: pertenencia a familias conocidas, perfil filogenético (presencia en otros organismos), pertenencia a operones o clusters de genes (genes que se presentan agrupados en diferentes organismos, lo que a menudo tiene implicaciones funcionales), etc. La información comparativa puede incluso ayudarnos a predecir la función para ORFs de funcion desconocida en el organismo que analizamos: comparando diversos organismos podemos conocer aquellos genes/proteínas que realicen funciones esenciales y que no hayan sido descubiertas en este. Las bases de datos de metabolismo son de considerable ayuda en este punto. La información posicional tambien es muy importante: la función de algunos ORFs puede conocerse de acuerdo a su vecindad con ORFs de función conocida, si esta disposición esta conservada en diferentes organismos.
Algunas bases de datos especialmente orientadas al estudio comparativo de genomas son:
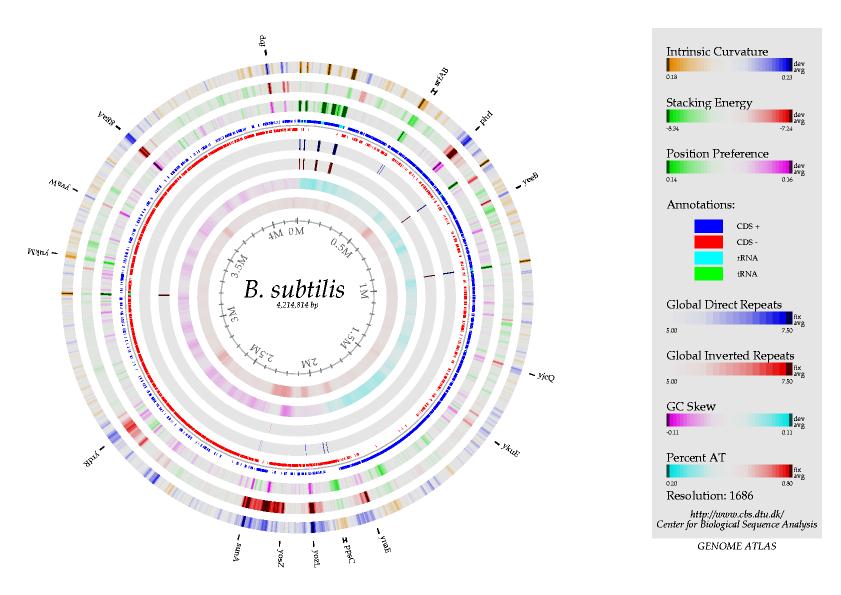
COGs. Esta base de datos del NCBI consiste en unas 2800 familias de proteinas conservadas o COGs, que contienen grupos de proteínas ortólogas. Por definición, dos proteínas, o genes, son ortólogos si han evolucionado a partir de un mismo ancestro. Tipicamente, genes o proteinas ortólogas tienen la misma función; no tiene por que ocurrir lo mismo entre genes o proteínas parálogas, que en vez de haber sido originadas por especiación (divergencia entre especies), han sido originadas por duplicación de un gen y posterior evolución hasta, a veces, desarrollar una nueva funcionalidad. Dado que cada COG incluye proteinas de organismos filogenéticamente muy diversos, este sitio es especialmente útil para asignar función a proteínas que no muestran un grado significativo de similaridad con otras proteínas. Para ello, el usuario tiene la posibilidad de enviar secuencias a traves del interfaz COGnitor, que serán analizadas y asignadas a alguno de los COGs existentes. Otras herramientas disponibles en COGs permiten analizar la distribución de genes en genomas (Phylogenetic patterns) o analizar semejanzas entre genomas mediante análisis de componentes principales. KEGG. Esta es la Kyoto Enciclopedia of Genes and Genomes, y está centrada fundamentalmente en la comparación de genomas en cuanto a su capacidad para codificar diferentes rutas metabólicas. El usuario puede obtener mapas metabólicos e identificar qué enzimas están presuntamente codificadas por un genoma en concreto. Otro tipo de análisis posible con KEGG es la identificación de clusteres de genes (o grupos de genes consecutivos) conservados entre dos especies. MBGD. La Microbial Genome Database es otro sitio muy util para identificar genes o proteinas homólogas, en varios genomas. PEDANT es un sistema para análisis de genomas. Aunque no es accesible desde el exterior (no podemos analizar nuestras secuencias), si podemos examinar los análisis ya realizados para gran cantidad de organismos, incluso algunos aun no completos. DNA Structural Atlas. En esta pagina web se recoge el análisis estructural de muchos de los genomas procarioticos secuenciados. Es posible acceder a una serie de datos estadísticos (contenido A+T, densidad de genes, etc) y a una serie de atlas o mapas circulares en los que se representa la medida de muchos parámetros (curvatura, secuencias repetidas, palíndromes, etc), como el que se ve en la figura siguiente.